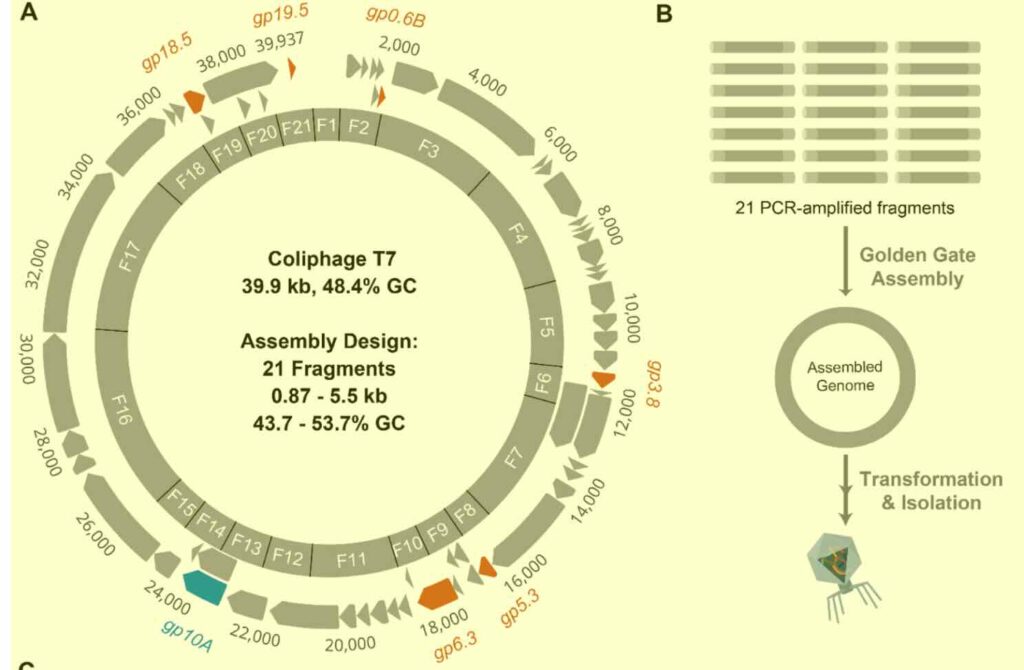
In deze methode wordt stukjes faag-DNA letter voor letter ‘opgebouwd’ waarna de DNA-stukken (hier 21) aaneen worden ‘gelast’. Rechtsonder de uieindelijke faag. (afb: Andy Sikkema et al./ACS Synthetic Biology)
Onderzoekers van New England Biolabs (NEB) en de Yale-universiteit zouden het eerste volledig kunstmatige systeem hebben ontwikkeld voor het ‘bouwen’ van bacteriofagen (letterlijk bacterievreters) voor Pseudomonas aeruginosa. Die bacterie is over de hele wereld ongevoelig geworden voor antibiotica en dat is niet goed (voor de mens, die overigens zelf heeft gezorgd voor die resistentie). Daarbij is het HC-GGA-platform van NEB gebruikt. Daarmee kunnen onderzoekers bacteriofagen ‘bouwen’ met behulp van DNA-sequenties in plaats van het assembleren van (grotere) stukken bestaand DNA-erfgoed. Lees verder